TASSEL进行GWAS分析
一开始折腾的是GAPIT,可是老是报错,实在是没办法了,就折腾TASSEL.
参考文献
下载安装
直接从https://tassel.bitbucket.io/下载安装即可。
数据准备
基因型文件
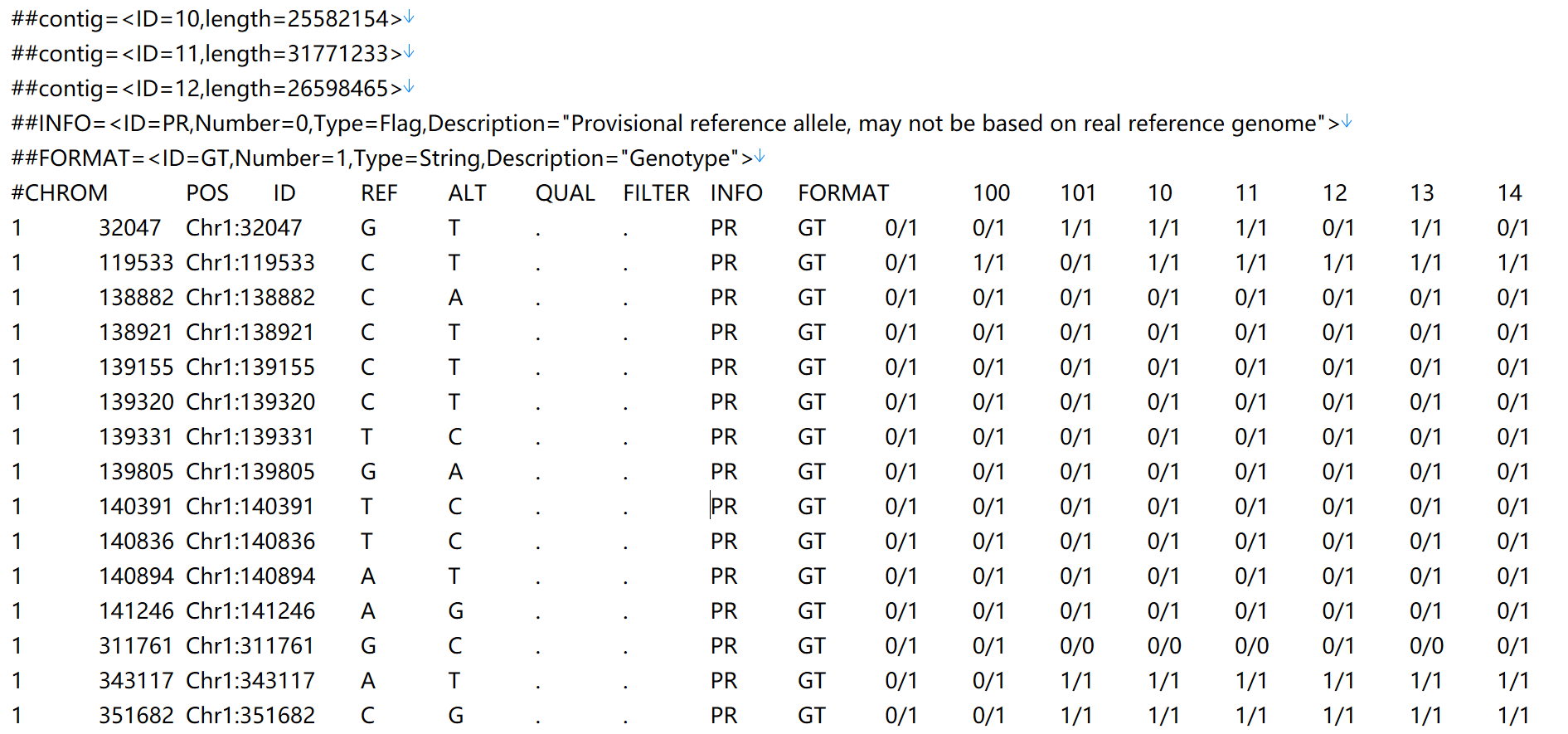
一开始准备了各种文件,但是一直报错,索性就直接用VCF文件了:
表型文件
表型文件前面需要加上<Trait>,第二列就是表型名称。

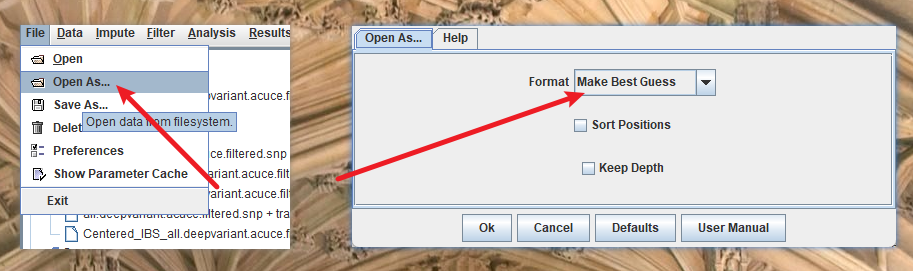
导入文件
选择这个模式就会自动识别数据类型。
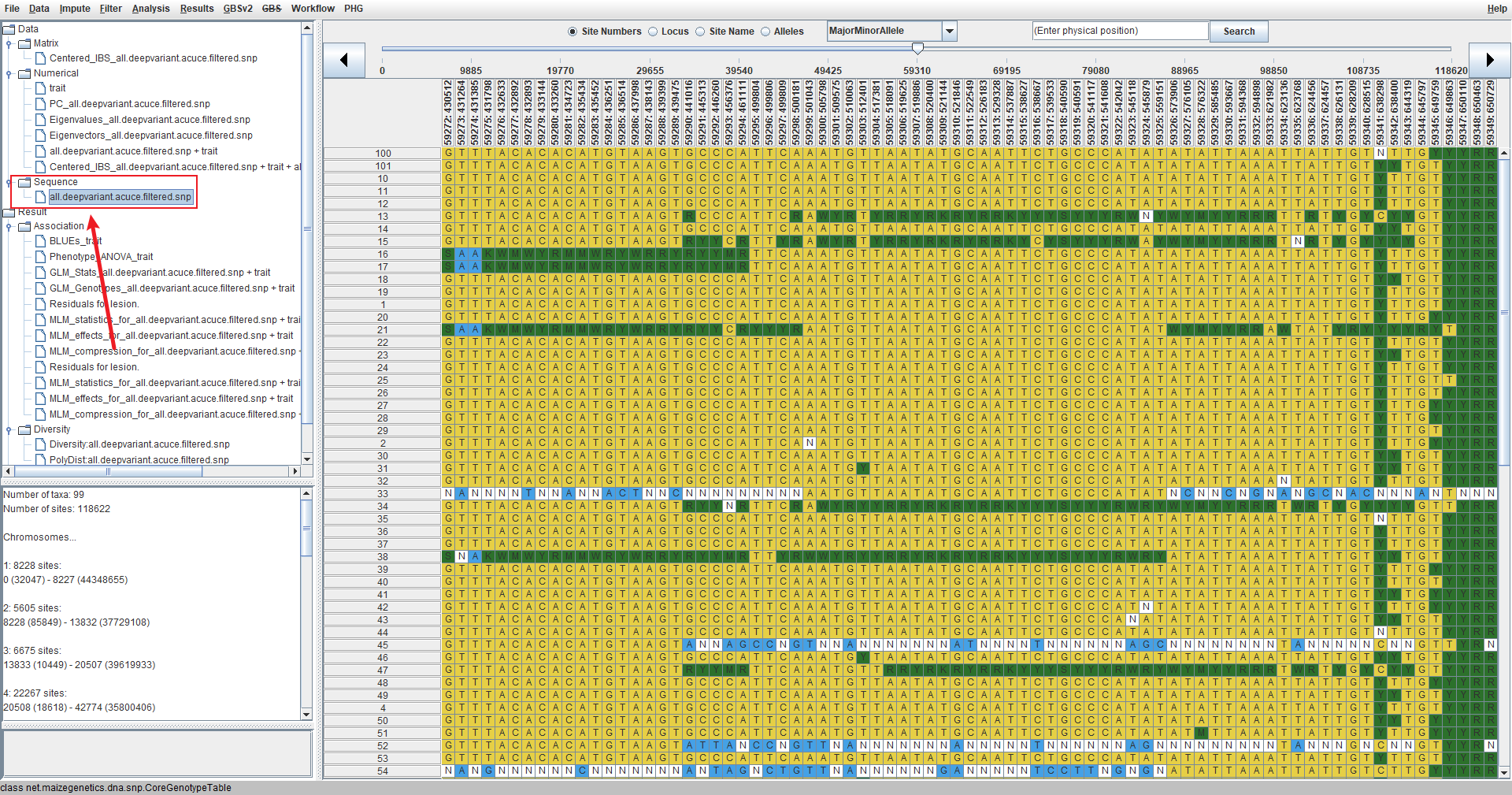
基因型文件长这样:
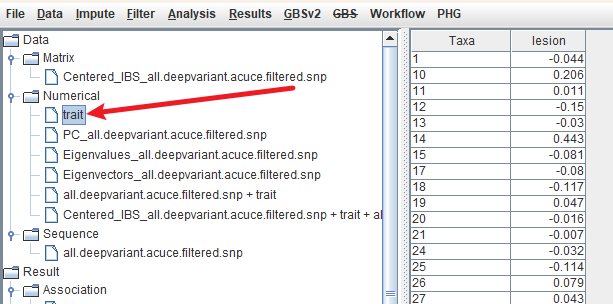
表型文件长这样:
同时选中基因型文件和表型文件,选择Data中的数据合并就能将两个数据合并为一个:
GLM
选择上一步中合并得到的文件,选择Analysis中的GLM就能使用GLM进行GWAS分析。选中得到的结果文件,选择Results中的Q-Q图和曼哈顿图就能得到这两个图形:
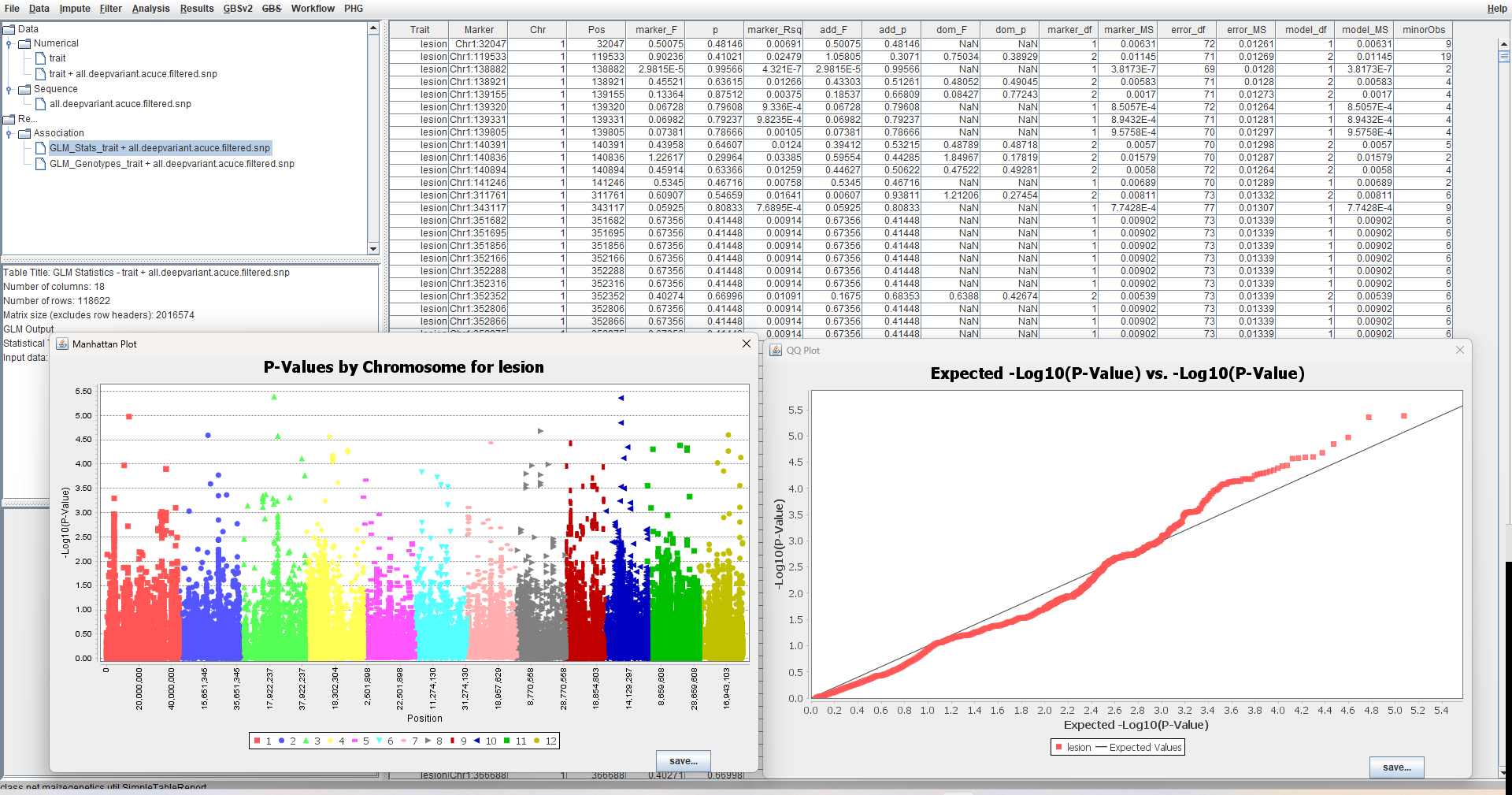
MLM
在使用MLM之前需要先构建Kinship,选中基因型文件,再选择Analysis中的Kinship就能得到Kinship.

选中之前合并的基因型文件和表型文件,再选中生成的Kinship矩阵就能使用MLM进行GWAS分析了:
可视化
得到结果表格后就可以使用ggplot2对数据进行可视化了。
TASSEL进行GWAS分析
https://lixiang117423.github.io/article/tasselgwas/