参考文献
Wilkinson S W, Hannan Parker A, Muench A, et al. Long-lasting memory of jasmonic acid-dependent immunity requires DNA demethylation and ARGONAUTE1[J]. Nature Plants, 2023: 1-15.
原始数据:点击查看
参考基因组 Ensembl Plants TAIR10.55
软件安装
1 mamba install -c bioconda bismark
1 2 3 4 wget -c https://nchc.dl.sourceforge.net/project/bowtie-bio/bowtie2/2.5.1/bowtie2-2.5.1-linux-x86_64.zip
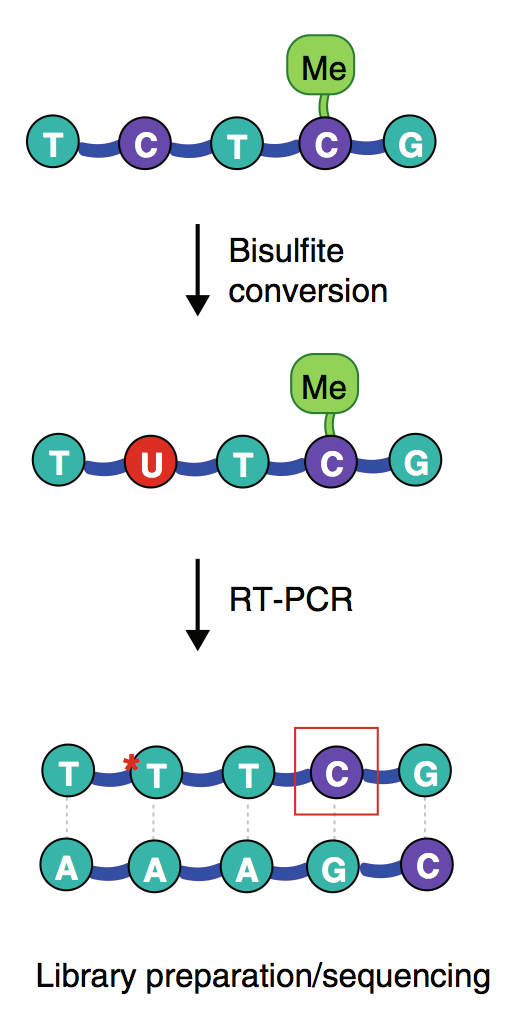
基因组准备 甲基化的C在Bisulfite处理后不会发生变化;未发生甲基化的C在处理后会变为U,PCR扩增后会变为T. 因此甲基化比对时需要特定的基因组,所以需要对基因组进行转换:C->T 和 G->A.
DNA甲基化比对使用最广泛的比对软件是Bowtie2,因此选择Bowtie2作为比对器(不同的比对软件需要不同的index文件):
1 bismark_genome_preparation --path_to_aligner ~/mambaforge/envs/tools4bioinf/bin/ --bowtie2 --parallel 60 --verbose data/genome
完成转换后会在基因组数据路径下生成新的文件,分别是C->T 和 G->A的转换版:
1 2 3 4 5 6 7 8 9 10 11 12 13 14 15 16 17 18 19 20 21 22 ./data/genome
比对 1 bismark -p 60 --bowtie2 --genome ./data/genome/ -1 ./data/fastq/SRR18508333_1.fastq.gz -2 ./data/fastq/SRR18508333_2.fastq.gz -o ./results/2.mapping
去重 1 deduplicate_bismark --bam results/2.mapping/SRR18508333_1_bismark_bt2_pe.bam
甲基化提取 1 bismark_methylation_extractor --gzip --bedGraph results/2.mapping/SRR18508333_1_bismark_bt2_pe.deduplicated.bam -o results/2.mapping